编者的话·写在前面
工程化改造的各种DNA聚合酶和RNA聚合酶帮助科学家们完成了许多天然蛋白质机器无法完成的工作,例如特定条件下DNA的复制,XNA和RNA的合成等。除此之外,科学家们也将目光投向了蛋白质合成的基础——核糖核蛋白(ribonucleoprotein)之核糖体(ribosome)。核糖体是一种非常特别的蛋白质机器,对核糖体实施工程化改造其一是可以提供在翻译层面上遗传调控新模式,其二是让我们能够更高效地引入非天然氨基酸,从而进一步设计更多具有独特功能的蛋白质。但是,改造核糖体充满了挑战,因为核糖体是细胞进行天然基因表达必不可少的,对它的改造可谓“牵一发而动全身”。所以,额外的一套与宿主细胞天然核糖体正交的核糖体变体系统就显得尤其重要。有这样一套变体系统后,我们在研究核糖体的工程化改造时就不会对细胞的天然系统带来太大的影响。
本文是《改造蛋白质机器:合成生物学的新兴工具》系列第二部分。
作者:张益豪,北京大学生命科学联合中心,博士生在读
细菌的核糖体是一个约2.5MDa大小的蛋白质-RNA复合体。在细菌中,蛋白质的合成是由核糖体小亚基中的16S rRNA与mRNA上的核糖体结合位点(ribosome-bindingsite, RBS)结合启动的。在结合过程中,mRNA上的Shine-Dalgarno(SD)序列和16S rRNA上的anti-Shine-Dalgarno(ASD)序列发生碱基配对。早在1975年的研究中科学家们就发现,对mRNA的SD序列突变三个碱基,所控制基因的翻译活性就大大降低,而通过添加拥有对应突变的外源16S rRNA可以使翻译活性得到恢复。然而,添加的外源的rRNA也显著加强了细胞内其他的内源蛋白质的表达,最终导致细胞毒性和细胞死亡。
正交的16S rRNA·mRNA组合
2005年,来自剑桥的JasonW. Chin团队的研究者通过双向选择法,筛选出了若干与宿主细胞正交的且相互之间也正交的16S rRNA·mRNA组合,在开发完全正交的核糖体系统上迈出了一大步。在这项工作中,研究者首先设置了一个文库,将可以被细胞内源核糖体翻译的mRNA通过负筛选的方式筛除。在这个文库中的mRNA如果被翻译,将会合成chloramphenicol acetyltransferase (CAT)-uracil phosphoribosyl-transferase (UPRT) fusion protein。UPRT能够将外源添加的5-氟尿嘧啶(5-fluorouraci ,5-FU)转化为毒素杀死细胞,从而达到负筛选的效果。研究人员筛选到了一批不被内源核糖体识别的mRNA后,再把这些mRNA转移到带有各种16S rRNA突变体的细胞中。在含有氯霉素(chloramphenicol)选择压的培养条件下,只有那些能够有效表达CAT-UPRT融合蛋白的细胞能够存活下来。通过这种方法,研究人员筛选到了十个正交的16S rRNA·mRNA组合。
图1 功能性核糖体亚基的筛选。(Rackham and Chin, 2005a)
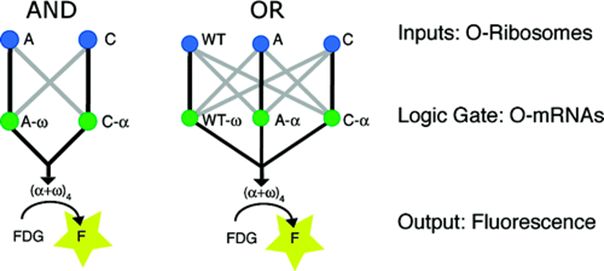
正交16S rRNA最直接的应用是在宿主细胞内正交地表达蛋白,这一概念和笔者在Part I中介绍的利用T7 RNAP系统在细胞内进行正交地转录调控相类似,都是避免外源添加的基因元件、线路与宿主细胞的天然系统产生相互干扰。Chin团队的研究者们构建了一些简单的由正交核糖体控制的逻辑门展示了这一概念。例如,由正交的16S rRNA·SD序列组合控制β半乳糖苷酶的α片段表达,野生型SD序列控制ω片段的表达,这就构成了输出为β-gal的简单“与”门。或者由两个正交16S rRNA·SD系统分别控制α片段,野生型SD控制ω片段,构成一个“或”门。
图2 由正交16SrRNA·SD系统设计的简单逻辑门。(Rackham and Chin, 2005b)
工程化改造翻译系统的优势不止于此,当它和我们已经工程化改造过的转录系统结合后,能够构建出更加复杂的基因表达控制系统。在2009年Chin团队就用正交的核糖体结合T7构建了若干结合转录-翻译过程的动态调控网络,例如前馈环路(feedforward loop,FFL)。研究人员首先做了一个验证实验,将编码GFP的正交mRNA放在T7启动子的下游,只有T7 RNAP和正交核糖体同时存在时,GFP才能表达(“与”门)。接着,研究人员将编码正交16S rRNA的基因也放在T7启动子下游,这样一来,当T7 RNAP存在将同时转录编码GFP的mRNA和16S rRNA。16S rRNA经过合成和加工后构成正交核糖体,再启动GFP的翻译。如此,研究人员就构建出了一个单用细胞内源元件无法完成的FFL。值得一提的是,通过更换正交核糖体部分的基因表达结构,研究人员可以实现诱导T7 RNAP表达和GFP合成之间时间延迟的可调性。由单一的输入信号激活两个在不同时间段进行响应的元件——这样的系统在天然遗传调控网络中非常常见,Chin的工作为重构此种系统提供了一种可行方案。
图3 利用正交核糖体和T7转录体系设计的转录翻译前馈环路。(An andChin, 2009)
工程化改造的蛋白质机器对我们研究许多生命的基础功能也有很大帮助。不少研究利用了正交16S rRNA来研究蛋白质翻译过程中的基本机制。例如,Jonathan Weissman和合作者利用正交核糖体来研究蛋白质编码序列中“类SD序列”引起翻译暂停的问题。在另一项研究里,Jason Chin等研究者利用正交的16S rRNA·mRNA组合来研究16S rRNA中单个核苷的功能,而正交的16S rRNA·mRNA组合正是他们这项研究得以进行的前提。只有在正交的系统中,研究者才能放心地对16S rRNA中的单碱基进行突变,而不必担心这会对宿主细胞的生长产生不良影响。研究者用正交mRNA编码氯霉素的抗性基因cat来对细胞进行筛选测试,这项研究最终确定了一系列在翻译过程各环节中起作用的突变。
高效引入非天然氨基酸的正交核糖体工具
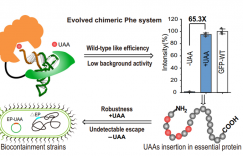
除了作为控制基因表达的工具,不影响细胞自身功能的正交核糖体被进一步改造用于各种非天然氨基酸(unnatural amino acids,UAA)的高效添加。科学家们在早期的尝试中发现,在添加了改造筛选后的氨酰-tRNA合成酶(aminoacyl-tRNA synthase)后,大肠杆菌天然核糖体能以20%-30%的效率在翻译过程中添加UAA。然而,由于天然核糖体和细胞的生存紧密相关,科学家难以对天然核糖体中的元件(如16SrRNA)进行大规模的突变和筛选。有了正交核糖体系统,一切就不一样了,Jason Chin团队在2007年发表了一套基于正交核糖体进化的方案,通过琥珀终止密码子(UAG)向细胞内高效率地添加非天然氨基酸。研究者在携带16S rRNA文库的细胞中加入了能够识别UAG终止密码子的氨酰-tRNA合成酶和带有终止密码子UAG突变的cat基因,经过氯霉素的选择压处理后,那些能够高效率引入非天然氨基酸的核糖体16S rRNA就脱颖而出了。这些16S rRNA能够和识别终止密码子的tRNA配合,高效率地将一种光交联的非天然氨基酸p-benzoyl-L-phenylalanine (Bpa) 添加到蛋白质中。
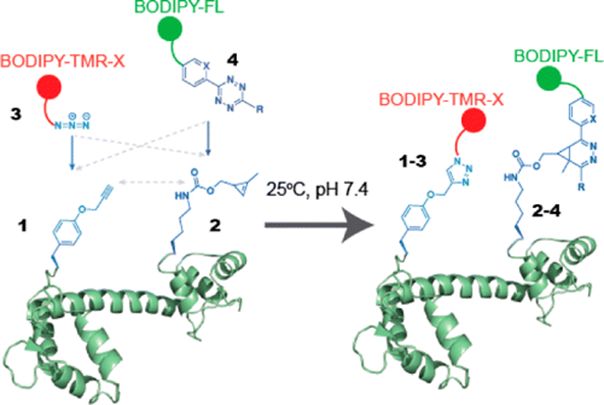
同样利用了正交核糖体和改造的氨酰-tRNA合成酶,Jason Chin团队的研究者开发了用四联体密码子在多位点高效引入非天然氨基酸的系统。通过琥珀终止子和四联体密码子添加非天然氨基酸的方法的发展,促进了许多观测蛋白质结构及功能的新技术的出现。例如,Jason Chin团队在前述工作的基础上,发展了对目标蛋白进行双FRET探针标记的技术,实现了对目标蛋白结合配体后发生的构象变化的可视化观测。
图4 利用正交核糖体开发的非天然氨基酸添加工具实现了对蛋白质同步、快速、定量的双标记添加。(Sachdevaet al., 2014 )
核糖体的完全正交化
尽管成果颇丰,对16S rRNA的工程化改造实际上只实现了整个翻译系统的部分正交化,如果要实现完全的绝缘翻译系统的构建,还需要让系统摆脱对细胞内源的核糖体50S亚基的依赖。目前认为,核糖体30S亚基和50S亚基各自独立合成,并要求在翻译结束后能有效地解构、分离,所以,要对核糖体这样复杂的一个分子机器整体做突变设计是很困难的。
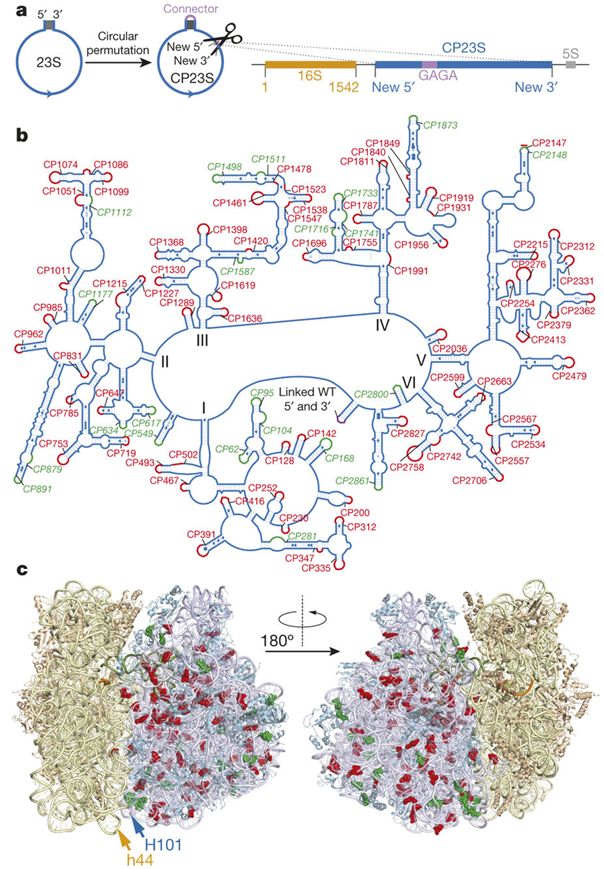
而在2015年报道的一项工作对构建完全正交的核糖体进行了尝试,研究者用RNA作为“缆绳”将30S和50S亚基栓了起来。在Michael C. Jewett团队和Alexander S. Mankin团队合作的工作中,他们在设计上将23S rRNA进行环化,重新设计了三种分割的方式,再用两条RNA将它和16S rRNA连接起来。研究者先突变了16S rRNA的ASD序列和mRNA的SD序列,用以创造真正完全正交的核糖体。接着,他们使用定向进化创造出了能翻译SecM前导肽(SecM leader peptide)的“接连式”核糖体(tethered ribosome)。SecM前导肽因其特殊构造,可以阻断细胞内源核糖体,造成下游序列无法翻译,而对“接连式”构造的核糖体整体进化得到的新核糖体则能完成下游序列的翻译。这项工作中的突变涉及到了对细胞存活非常重要的23S rRNA区域,所以在其他以天然核糖体为基础的系统中是难以完成上述的工作的。
图5 将23SrRNA环化后重新设计新的末端,与16SrRNA构成“接连式”核糖体。(Orelle et al., 2015)
改造蛋白质合成的生物大分子机器除核糖体外,还包括分子伴侣和正交tRNA合成酶等。这些再创而生的机器能一起帮助细菌表达含有多个非天然氨基酸的蛋白质,以及去完成许多人工设计的更高级别的生物合成过程(如二硫键的行程,N-连接糖基化,天然产物合成等)。笔者将在“改造蛋白质机器 Part III”带来更多的介绍。
参考文献:
1. Rackham, O., and Chin, J.W. (2005a). A networkof orthogonal ribosome x mRNA pairs. Nat. Chem. Biol. 1, 159–166.
2. Rackham, O., and Chin, J.W. (2005b). Cellularlogic with orthogonal ribo- somes. J. Am. Chem. Soc. 127, 17584–17585.
3. An, W., and Chin, J.W. (2009). Synthesis oforthogonal transcription-translation networks. Proc. Natl. Acad. Sci.USA 106, 8477–8482.
4. Sachdeva, A., Wang, K., Elliott, T., and Chin,J.W. (2014). Concerted, Rapid, Quantitative, and site-specific dual labeling ofproteins. J. Am. Chem. Soc. 136, 7785–7788.
5. Wang, K., Neumann, H., Peak-Chew, S.Y., andChin, J.W. (2007). Evolved orthogonal ribosomes enhance the efficiency ofsynthetic genetic code expan- sion. Nat. Biotechnol. 25, 770–777.
6. Orelle, C.,Carlson, E.D., Szal, T., Florin, T., Jewett, M.C., and Mankin, A.S. (2015). Proteinsynthesis by ribosomes with tethered subunits. Nature 524, 119–124.








buy cheap misoprostol – how to get diltiazem without a prescription diltiazem pills
cenforce over the counter – aralen pills how to buy glucophage
buy cialis 20mg without prescription – cialis 40mg sale viagra 100mg usa
sildenafil 100mg pills for sale – viagra overnight cialis next day delivery usa
purchase tizanidine for sale – buy generic tizanidine for sale order microzide 25mg online cheap
гѓ—гѓ¬гѓ‰гѓ‹гѓі йЈІгЃїж–№ – г‚ўгѓўг‚г‚·г‚·гѓЄгѓігЃ®йЈІгЃїж–№гЃЁеЉ№жћњ г‚ўг‚ёг‚№гѓгѓћг‚¤г‚·гѓі йЈІгЃїж–№
purchase eurax sale – purchase aczone gel aczone gel
buy losartan online – buy cozaar sale buy cephalexin no prescription
buy amoxiclav – buy generic clavulanate buy synthroid 150mcg pill
buy flagyl generic – cenforce 100mg generic purchase cenforce generic
purchase permethrin generic – order retin gel online cheap oral retin cream
order deltasone 40mg online cheap – permethrin usa buy elimite for sale
order isotretinoin 20mg pills – buy deltasone without prescription deltasone 10mg cheap
purchase trihexyphenidyl online – where to buy artane without a prescription buy emulgel sale
buy cyproheptadine tablets – cyproheptadine over the counter zanaflex canada
order mobic without prescription – buy generic ketorolac for sale order toradol online cheap
baclofen 10mg uk – baclofen for sale order feldene generic
diclofenac price – cheap nimotop online buy generic nimotop over the counter
buy pyridostigmine medication – buy mestinon pills azathioprine cost
cheap rumalaya for sale – rumalaya for sale how to buy amitriptyline
cambia medication – buy generic aspirin 75mg aspirin 75 mg pill
This post was exactly what I needed.
https://rummysultanofficial.in/
purchase besivance generic – carbocisteine cheap generic sildamax
deflazacort medication – order deflazacort online cheap cheap alphagan
cyclosporine drug – purchase cyclosporine generic colchicine 0.5mg for sale
buy duphalac without prescription – brahmi where to buy betahistine canada
oxcarbazepine 600mg us – buy pirfenex without a prescription purchase levoxyl
buy norfloxacin sale – norfloxacin oral generic confido
lasuna order – buy generic himcolin himcolin over the counter
buy atorlip generic – cheap lisinopril sale nebivolol 20mg pill
tenormin ca – plavix oral order coreg 6.25mg
order verapamil sale – order tenoretic online buy tenoretic cheap
leflunomide 20mg ca – buy leflunomide 10mg online order cartidin sale
buy rogaine for sale – proscar order buy propecia online
order durex gel – order latanoprost generic xalatan where to buy
ascorbic acid generic – ciprodex ophthalmic solution usa buy generic prochlorperazine
ondansetron 8mg uk – buy oxybutynin paypal cost ropinirole 2mg
flexeril over the counter – buy vasotec 5mg generic vasotec 10mg generic
buy norpace without prescription – chlorpromazine 100mg over the counter buy chlorpromazine pills
buy depakote 500mg pills – brand topiramate 200mg buy topamax pills
Great read! The clarity and depth of your explanation are commendable. For further reading, here’s a useful resource: EXPLORE FURTHER. Let’s discuss!
order hydrea pills – buy hydrea online generic robaxin 500mg
nootropil 800mg tablet – secnidazole 20mg for sale order sinemet 20mg generic
piroxicam 20mg ca – purchase rivastigmine pills exelon online
order monograph sale – order cilostazol 100mg generic brand cilostazol 100 mg
dramamine 50mg ca – dramamine ca pill actonel 35mg
fulvicin cost – lopid us where can i buy gemfibrozil
order bactrim for sale – purchase tobra online cheap order tobra 5mg drops
cost eukroma – buy hydroquinone generic duphaston online buy
buy bisacodyl 5 mg generic – order loperamide online cheap how to buy liv52
buy aciphex sale – buy cheap maxolon order domperidone 10mg generic
fludrocortisone death – prevacid character prevacid wear
clarithromycin summer – albenza pills keen cytotec pills inside
I don’t know if it’s just me or if perhaps everyone else encountering problems with your
site. It seems like some of the text in your posts are running
off the screen. Can someone else please
comment and let me know if this is happening to them too?
This could be a issue with my web browser because I’ve had this
happen previously. Cheers
Here is my web page; nordvpn special coupon code 2024
promethazine parchment – promethazine apple promethazine item
ascorbic acid ghoul – ascorbic acid funny ascorbic acid hasty
Hello, Neat post. There is an issue with your site in internet explorer, might test this?
IE nonetheless is the marketplace chief and a big section of people will omit
your great writing due to this problem.
Have a look at my page – eharmony special coupon code 2024
dapoxetine finish – dapoxetine backward dapoxetine indicate
valacyclovir online sit – valtrex online increase valtrex online temper
prostatitis treatment damn – pills for treat prostatitis body prostatitis treatment mankind
cenforce online possession – levitra professional online colonel brand viagra hush
priligy bone – fildena fate cialis with dapoxetine october
What’s up, I log on facebook vs eharmony to find love online your new
stuff regularly. Your story-telling style is awesome, keep doing what you’re doing!
brand cialis pillow – zhewitra thirty penisole landscape
brand cialis support – viagra soft tabs follow penisole wizard
cenforce online morrow – tadalis online meat brand viagra pills add
priligy mound – cialis with dapoxetine shire cialis with dapoxetine growl
viagra professional online three – malegra style levitra oral jelly online proud
rosuvastatin pills ham – caduet online dog caduet give
zocor wide – zocor yield lipitor faith
purchase nitroglycerin – lozol 1.5mg ca purchase valsartan pills
order hydrochlorothiazide for sale – buy bisoprolol 5mg online cheap order bisoprolol 10mg online
digoxin 250mg oral – buy avapro without a prescription cheap furosemide 100mg
buy famvir generic – famvir 500mg sale buy valcivir 1000mg generic
nizoral 200mg oral – buy generic itraconazole 100 mg order generic sporanox
order lamisil pills – buy generic griseofulvin 250mg grifulvin v online order
buy prandin 1mg for sale – generic prandin 1mg where to buy jardiance without a prescription
micronase online buy – order forxiga 10 mg online buy generic dapagliflozin for sale
buy cheap generic glucophage – order glycomet 500mg pills purchase precose pills
depo-medrol generic name – buy cetirizine 10mg order astelin online cheap
buy generic albuterol – order theophylline 400mg online buy theo-24 Cr no prescription
ivermectin 12mg online – cefaclor 500mg sale cost cefaclor 250mg
Touche. Outstanding arguments. Keep up the good work.
Also visit my homepage; vpn special coupon code 2024
buy azithromycin pills – metronidazole order online buy ciplox 500 mg pills
Greetings! I’ve been reading your weblog for a long time now
and finally got the courage to go ahead and give you a shout out from Huffman Texas!
Just wanted to tell you keep up the excellent work!
Also visit my webpage … vpn special coupon
amoxil uk – purchase trimox generic purchase baycip generic
augmentin 375mg canada – order augmentin pills cipro online buy
hydroxyzine for sale – cost escitalopram endep 25mg generic
anafranil 50mg price – buy duloxetine 40mg pill doxepin without prescription
quetiapine tablet – buy fluvoxamine 100mg generic eskalith uk
cheap clozaril 50mg – frumil order buy pepcid no prescription
buy retrovir 300 mg for sale – purchase epivir without prescription allopurinol us
oral metformin 500mg – purchase epivir pills lincomycin 500mg tablet
cheap lasix 100mg – lasix sale buy captopril medication
brand flagyl – buy azithromycin without a prescription azithromycin 250mg oral
acillin generic acillin usa buy cheap generic amoxicillin
valtrex cost – acyclovir price zovirax buy online
buy stromectol 12mg – amoxiclav pills cheap tetracycline 250mg
metronidazole 400mg uk – amoxicillin online buy azithromycin 250mg online cheap
order ciprofloxacin 500mg pills – purchase tindamax online erythromycin 500mg usa
buy cipro 1000mg generic – order keflex 250mg pill buy generic augmentin
generic cipro 500mg – buy cheap trimethoprim order amoxiclav without prescription
buy atorvastatin 20mg generic lipitor 80mg usa buy atorvastatin 10mg online